01/04/2022
AllCCS: En revolution inden for metabolomik
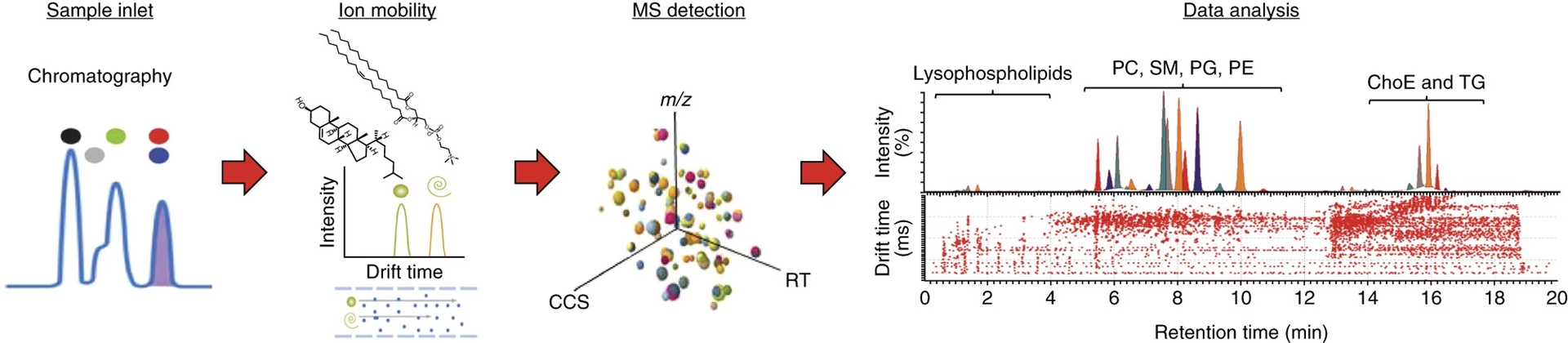
Metabolomik, studiet af små molekyler i biologiske systemer, er et hurtigt voksende felt, der har potentiale til at revolutionere vores forståelse af biologi og sygdom. Et centralt aspekt af metabolomik er evnen til præcist at identificere og kvantificere et bredt spektrum af metabolitter, både kendte og ukendte. Traditionelle metoder har ofte stået over for udfordringer med hensyn til nøjagtighed, dækning og evnen til at håndtere den iboende kompleksitet af biologiske prøver. Nyere teknologier, især dem der integrerer ionmobilitet-massespektrometri (IM-MS), lover dog at overvinde disse begrænsninger. I hjertet af denne teknologiske udvikling ligger databaser og prædiktionsværktøjer, der er designet til at udnytte den fulde potentiale af IM-MS. En af de mest lovende udviklinger på dette område er lanceringen af AllCCS-databasen, en omfattende ressource, der sigter mod at standardisere og dele eksperimentelle og forudsagte CCS-værdier (Collision Cross Section) for et stort antal små molekyler.
Hvad er CCS og hvorfor er det vigtigt i Metabolomik?
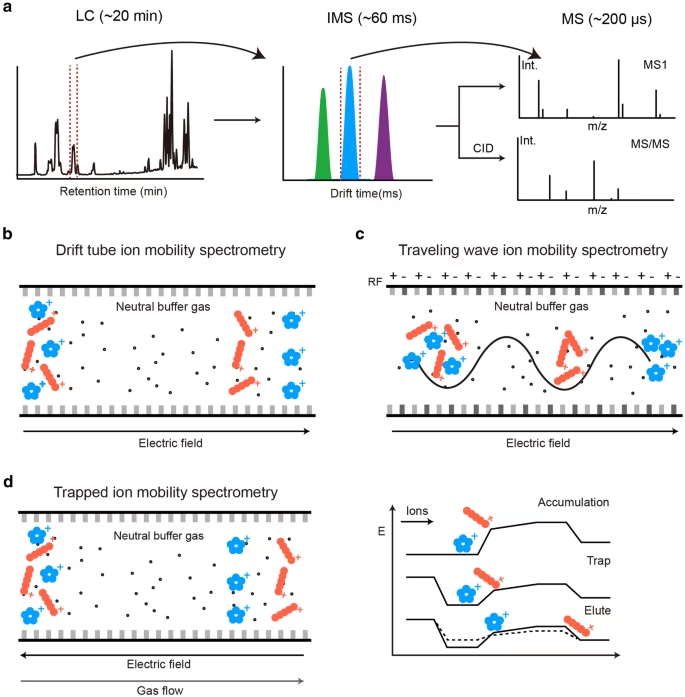
Kollisionskvadrat (CCS) er et mål for størrelsen og formen af et ion i gasfasen. I forbindelse med IM-MS giver CCS-værdien en ekstra dimension af information ud over masse-til-ladningsforholdet (m/z) og retentionstiden (RT). Denne ekstra dimension er afgørende for at forbedre nøjagtigheden af metabolitidentifikation. Tænk på det som at tilføje en unik tredimensionel signatur til hver metabolit. Mens m/z og RT kan være ens for forskellige forbindelser, er deres CCS-værdier ofte distinkte. Ved at integrere CCS-målinger i analyseprocessen kan forskere markant reducere antallet af potentielle kandidater, når de forsøger at identificere ukendte metabolitter eller bekræfte kendte metabolitter i komplekse biologiske matricer.
AllCCS-databasen: En Enorm Ressource
AllCCS-databasen repræsenterer et betydeligt fremskridt inden for indsamling og organisering af CCS-data. Databasen er bygget på en robust proces, der involverer indsamling af tusindvis af eksperimentelle CCS-værdier fra forskellige kilder, herunder flere laboratorier og kommercielle IM-MS-instrumenter. Disse data gennemgår en streng standardiseringsprocedure for at sikre ensartethed og nøjagtighed.
Standardisering og Kvalitetskontrol
Processen for at skabe den 'enhedsgjorte' AllCCS-database omfatter flere kritiske trin:
- Indsamling af metainformation: Alle relevante detaljer om de eksperimentelle målinger indsamles.
- Kvalitetstjek: Data gennemgår en grundig kvalitetskontrol for at identificere og fjerne upålidelige målinger.
- Fjernelse af outliers: Ved hjælp af avancerede teknikker som trendlinjeanalyse fjernes afvigende værdier for at forbedre nøjagtigheden.
- Beregning af enhedsgjorte CCS-værdier: Standardiserede CCS-værdier beregnes.
- Tildeling af konfidensniveauer: Hver enhedsgjort CCS-værdi tildeles et konfidensniveau baseret på kvaliteten og mængden af understøttende eksperimentelle data.
Resultatet er en database med tusindvis af enhedsgjorte CCS-værdier for hundredvis af forbindelser, der dækker et bredt spektrum af kemiske strukturer og adduct-former. AllCCS adskiller sig fra andre databaser ved sin evne til at forene forskellige CCS-værdier og dermed overvinde variationer mellem forskellige instrumenter og laboratorier.
Kemisk Diversitet og Dækning
AllCCS-databasen er imponerende i sin kemiske diversitet. Den dækker et bredt udvalg af kemiske klasser og underklasser, herunder lipider, organheterocykliske forbindelser og benzenoider som de mest fremtrædende superklasser. Sammenlignet med andre databaser som Human Metabolome Database (HMDB) og DrugBank viser AllCCS en bemærkelsesværdig dækning af de kemiske rum, hvilket indikerer dens repræsentativitet og relevans for et bredt spektrum af metabolomik-studier.
CCS Prædiktion og Ydeevne Benchmarking
Ud over at indeholde eksperimentelle data, excellerer AllCCS også i at forudsige CCS-værdier for et endnu større antal molekyler ved hjælp af avancerede maskinlæringsalgoritmer. Disse algoritmer er trænet på den store og mangfoldige enhedsgjorte eksperimentelle CCS-database.
Nye Funktioner i AllCCS Prædiktion
AllCCS adskiller sig fra andre prædiktionsværktøjer som MetCCS ved flere nøglefunktioner:
- Stort Træningsdatasæt: Bruger et omfattende datasæt med høj kemisk diversitet.
- Reduceret Deskriptorsæt: Anvender et optimeret sæt af molekylære deskriptorer for øget effektivitet.
- RSS Score: Udvikler en 'Representative Structure Similarity' (RSS) score til at estimere prædiktionsnøjagtigheden.
Med over 1,6 millioner forbindelser og mere end 11 millioner forudsagte CCS-værdier er AllCCS den største og mest omfattende CCS-database, der er tilgængelig. Den dækker syv populære databaser, herunder KEGG, HMDB og DrugBank.
Validering og Præcision
Ydeevnen af AllCCS' prædiktionsmodel er blevet grundigt valideret ved hjælp af to uafhængige eksterne datasæt. Resultaterne viser en fremragende overensstemmelse mellem eksperimentelle og forudsagte CCS-værdier, med median relative fejl (MREs) så lave som 1,66% for metabolitter og lipider. Disse resultater bekræfter, at AllCCS kan forudsige CCS-værdier med høj nøjagtighed for både endogene og eksogene små molekyler.
Sammenligning med Konkurrenter
En benchmarking-analyse, der sammenligner AllCCS med andre værktøjer som MetCCS, DeepCCS og ISiCLE, afslørede, at AllCCS konsekvent leverer forbedret prædiktionsnøjagtighed. For eksempel opnåede 84% af CCS-værdierne i AllCCS en relativ fejl på under 4%, sammenlignet med lavere procenter for de andre værktøjer. AllCCS udviser også overlegenhed i dækning og anvendelighed, og leverer de bedste prædiktioner for de fleste kemiske superklasser.
Strukturel Lighed og Prædiktionsnøjagtighed: RSS Score
Et centralt fund fra udviklingen af AllCCS er, at nøjagtigheden af forudsagte CCS-værdier er stærkt afhængig af den strukturelle lighed mellem den inputtede kemiske struktur og træningsdatasættet. For at kvantificere dette forhold introducerede AllCCS en Representative Structure Similarity (RSS) score.
Hvordan RSS Virker
RSS-scoren, der beregnes ved hjælp af molekylær fingerprinting, spænder fra 0 til 1, hvor højere værdier indikerer større lighed med træningsdatasættet. Forskning har vist en stærk og signifikant korrelation mellem RSS-scorer og de relative fejl i CCS-prædiktioner. Molekyler med høje RSS-scorer udviser markant mindre fejl i deres forudsagte CCS-værdier.
Anvendelse af RSS i Praksis
Denne indsigt er afgørende for at forstå pålideligheden af forudsagte CCS-værdier. Ved at analysere RSS-scorer for forbindelser i almindelige databaser, fandt AllCCS, at over 80% af forbindelserne har høje eller medium RSS-scorer, hvilket indikerer, at AllCCS kan generere nøjagtige CCS-værdier for en stor del af kendte molekyler. Dette gør RSS til et værdifuldt værktøj til at vurdere og reflektere nøjagtigheden af CCS-prædiktioner, hvilket udvider AllCCS' brede anvendelighed.
Forbedret Annotering af Kendte Metabolitter
En af de mest umiddelbare anvendelser af AllCCS-databasen er dens evne til at forbedre annoteringen af kendte metabolitter. Ved at matche eksperimentelle m/z- og CCS-værdier med den store AllCCS-database kan forskere markant reducere antallet af potentielle kandidater.
Reduktion af Kandidater
Studier har vist, at integrationen af CCS-match kan reducere antallet af kandidater med op til 76% sammenlignet med metoder, der udelukkende baserer sig på m/z og retentionstid. Denne reduktion gælder også, når man bruger multi-dimensionelle match, der inkluderer MS/MS-spektra. AllCCS' evne til at filtrere kandidater er effektiv på tværs af forskellige databasestørrelser.
Forbedring af Rangering
Ud over at reducere antallet af kandidater forbedrer tilføjelsen af CCS-match også rangeringen af de korrekte kandidater. Dette betyder, at den rigtige metabolit oftere placeres højere på listen over potentielle identifikationer, hvilket sparer tid og øger tilliden til resultaterne. Dette er især tydeligt i eksempler, hvor korrekt identifikation af en metabolit med CCS-match forbedres fra 129. plads til 6. plads.
Anvendelse i Biologiske Prøver
Anvendelsen af multi-dimensionel match med CCS-data er blevet demonstreret i virkelige biologiske prøver, såsom muse-fibroblastceller og humane plasma. I disse analyser reducerede integrationen af CCS-match konsekvent antallet af kandidater, hvilket førte til mere pålidelig annotering af kendte metabolitter. Denne forbedring er især bemærkelsesværdig for lavt-abundante funktioner, hvor yderligere information som CCS kan være afgørende for identifikation.
AllCCS Muliggør Annotering af Ukendte Metabolitter
Måske den mest spændende anvendelse af AllCCS ligger i dens potentiale til at understøtte annoteringen af ukendte metabolitter. Disse er metabolitter, der ikke findes i eksisterende databaser, men som kan genereres gennem enzymatiske transformationer, biotransformationer eller mikrobielle processer.
Generering af Ukendte Metabolitter
Ved at bruge KEGG-databasen og simulere enzymatiske reaktioner har forskerne bag AllCCS udvidet det kendte kemiske rum til at omfatte over 100.000 mulige ukendte forbindelser. For alle disse genererede ukendte metabolitter er m/z-, CCS- og MS/MS-spektra blevet beregnet og forudsagt ved hjælp af AllCCS og andre værktøjer.
Multi-dimensionel Match for Ukendte
Denne udvidede database muliggør nu multi-dimensionel match-baseret annotering, der kan identificere både kendte og ukendte metabolitter i biologiske prøver. I muse-levervævsprøver blev et stort antal funktioner annoteret som ukendte metabolitter, hvilket giver et hidtil uset indblik i de ukendte komponenter i stofskiftet.
Karakterisering af Metabolisk Aktivitet
Integrationen af ukendte metabolitter i analyser har også muliggjort en dybere karakterisering af metabolisk aktivitet. Ved at analysere ændringer i både kendte og ukendte metabolitter i forbindelse med aldring hos mus, har forskerne kunnet identificere nedgange i specifikke stofskifteveje, herunder purinmetabolisme og aminosyrestofskifte. Bemærkelsesværdigt viste visse ukendte metabolitter mere signifikante ændringer end deres kendte forstadier, hvilket understreger vigtigheden af at inkludere disse hidtil ukendte forbindelser i studier.
Konklusion
AllCCS-databasen og dens tilhørende prædiktionsværktøjer repræsenterer en betydelig teknologisk landvinding inden for metabolomik. Ved at levere en standardiseret, omfattende og nøjagtig ressource til CCS-data, forbedrer AllCCS markant evnen til at identificere og kvantificere metabolitter, både kendte og ukendte. Dette åbner døren for dybere biologisk indsigt, forbedret sygdomsdiagnostik og udvikling af nye terapeutiske strategier. Fremtiden for metabolomik ser lysere ud end nogensinde med værktøjer som AllCCS i vores arsenal.
Ofte Stillede Spørgsmål (FAQ)
- Hvad er AllCCS-databasen?
- AllCCS er en omfattende database, der lagrer, standardiserer og deler eksperimentelle og forudsagte Kollisionskvadrat (CCS) værdier for små molekyler, primært til brug i ionmobilitet-massespektrometri (IM-MS).
- Hvorfor er CCS vigtigt i metabolomik?
- CCS giver en ekstra dimension af information ud over masse og retentionstid, hvilket forbedrer nøjagtigheden af metabolitidentifikation, især for ukendte forbindelser i komplekse prøver.
- Hvordan adskiller AllCCS sig fra andre CCS-databaser?
- AllCCS forener forskellige CCS-værdier fra flere kilder og instrumenter, hvilket overvinder variationsproblemer. Den har også en robust standardiseringsproces og en avanceret prædiktionsmodel med en unik RSS-score til at vurdere nøjagtighed.
- Kan AllCCS forudsige CCS-værdier for nye molekyler?
- Ja, AllCCS' maskinlæringsmodel kan forudsige CCS-værdier for nye forbindelser baseret på deres SMILES-struktur, med høj nøjagtighed, især for strukturer, der ligner dem i træningsdatasættet.
- Hvordan forbedrer AllCCS annoteringen af kendte metabolitter?
- Ved at integrere CCS-match i analyseprocessen reducerer AllCCS antallet af potentielle kandidater markant og forbedrer rangeringen af den korrekte identifikation, hvilket øger tilliden og effektiviteten af annoteringsprocessen.
- Hvad er fordelen ved AllCCS for ukendte metabolitter?
- AllCCS muliggør generering af en database med mulige ukendte metabolitter og deres forudsagte CCS- og MS/MS-spektra, hvilket understøtter deres identifikation og karakterisering i biologiske prøver, hvilket giver dybere indsigt i ukendte metaboliske processer.
Hvis du vil læse andre artikler, der ligner AllCCS: En revolution inden for metabolomik, kan du besøge kategorien Teknologi.